去年,DeepMind公司開發的AlphaFold2人工智能系統,基于氨基酸序列,精確預測了蛋白質的3D結構。它的準確性與使用冷凍電子顯微鏡(CryoEM)、核磁共振或 X 射線晶體學等實驗技術解析的3D結構相媲美。這一突破被譽為“變革生命科學和生物醫學”的突破。
今日,DeepMind公司在《自然》雜志上發表論文,公開了進一步優化的AlphaFold2人工智能系統的源代碼并且詳細描述了它的設計框架和訓練方法。同日,華盛頓大學(University of Washington)蛋白設計研究所David Baker教授課題組在《科學》雜志上發表論文,公布了其開源人工智能系統RoseTTAFold的研究結果。《自然》上發表的評論指出,這些論文和人工智能系統資源的發布,不但讓基于DeepMind開發的AI系統預測蛋白質結構的技術能夠為廣大科學家和研究人員使用,而且有望進一步激發這一領域的進展。
蛋白質對生命來說不可或缺,它們支持生物體的幾乎所有功能。這些復雜的大分子由氨基酸鏈構成,而蛋白質的功能很大程度上決定于它的3D結構。生物醫學領域的眾多挑戰,包括開發治療疾病的創新療法,依賴于對蛋白質結構和功能的理解。
在過去的五十年中,科學家們已經能夠利用冷凍電子顯微鏡、核磁共振或 X 射線晶體學等實驗手段在實驗室中確定蛋白質的形狀,但每種方法都依賴于大量的試錯,耗時耗力,可能需要花上好幾年時間。1972年,諾貝爾化學獎得主Christian Anfinsen博士表示,理論上,蛋白質的氨基酸序列應該能夠完全決定它的3D結構。這一假說激發了50年來基于氨基酸序列,通過計算方法預測蛋白質3D結構的探索。
在2018年,DeepMind開發的AlphaFold人工智能系統首次在國際蛋白質結構預測競賽(CASP)上亮相。而在去年的CASP上,DeepMind的AlphaFold2系統表現驚艷,在接受檢驗的近100個蛋白靶點中,AlphaFold2對三分之二的蛋白靶點給出的預測結構與實驗手段獲得的結構相差無幾。有些情況下,已經無法區分兩者之間的區別是由于AlphaFold2的預測出現錯誤,還是實驗手段產生的假象。
▲AlphaFold2根據氨基酸序列預測的蛋白結構與實驗手段解析的結果幾乎完全重合(綠色,實驗結果;藍色,計算預測結果;圖片來源:DeepMind Blog)
DeepMind今日發布的更新版AlphaFold2在去年的系統基礎上進行了優化,在解析蛋白結構的速度上有了進一步的提高。主要開發人員John Jumper博士說,這一系統的處理速度快了大約16倍。根據蛋白的大小,它可以在幾分鐘到幾小時內生成準確的蛋白結構。
AlphaFold2系統去年在CASP上的出色表現促進了蛋白質3D結構預測領域其它團隊的進步。華盛頓大學蛋白設計研究所David Baker教授的團隊從AlphaFold2的設計思路中獲得啟發,構建了名為RoseTTAFold的軟件系統。它的神經網絡能夠同時考慮蛋白序列的模式,蛋白中不同氨基酸之間的相互作用,以及蛋白質可能出現的3D結構。在這個系統中,一維、二維和三維的信息能夠相互交流,讓神經網絡綜合所有信息,決定蛋白質的化學組成部分和它折疊產生的結構之間的關系。
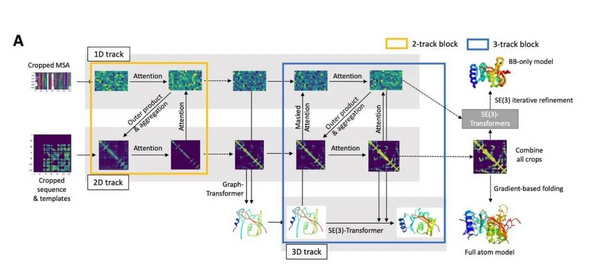
▲RoseTTAFold系統結構簡介(圖片來源:參考資料[3])
研究人員表示,RoseTTAFold系統在解析蛋白質3D結構方面的表現,與AlphaFold2的水平幾乎相當,在有些蛋白上甚至優于AlphaFold2。
在論文中,研究人員指出,這一工具還可以用于預測由兩個或者多個蛋白構成的復合體的構象。這讓研究人員可以直接從蛋白序列,推測出不同蛋白相互結合的結構模型。在論文中,研究人員利用IL-12和IL-12受體(IL-12R)的序列預測的IL-12/IL-12R復合體結構與此前用冷凍電子顯微鏡解析的結構非常類似。
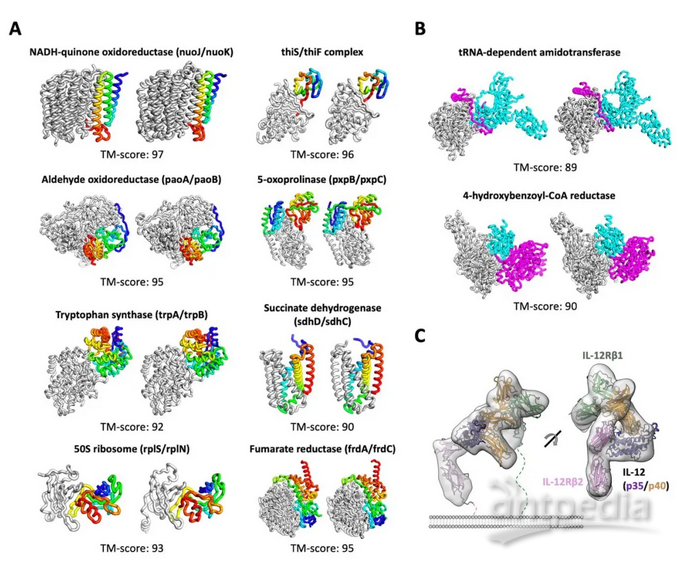
▲RoseTTAFold系統能夠基于多個蛋白序列,預測復合體的結構(圖片來源:參考資料[3])
Baker教授的團隊已經將RoseTTAFold軟件工具上傳到GitHub網站上,7月份以來,它已經被世界上超過140個不同研究團隊下載。
同時,該團隊也搭建了服務器,讓研究人員可以輸入蛋白質序列,然后獲得預測的蛋白結構。服務器在上個月啟動后,已經幫助解析了大約500名用戶遞交的超過5000個蛋白結構。“我很高興科學界已經在利用RoseTTAFold服務器來解決重要的生物學問題。” David Baker教授說。
“我們希望這一新工具將繼續為整個研發團體造福。”論文的第一作者,Baker教授課題組的博士后Minkyung Baek說。
《自然》發表的新聞評論指出,隨著RoseTTAFold和AlphaFold2源代碼的公布,研究人員可以在兩者的基礎上繼續前進,有望對人工智能系統做出進一步改進,攻克目前人工智能系統尚且無法確定構象的蛋白,以及使用這些軟件設計全新的蛋白。
我們期待這一天的早日到來。
參考資料:
[1] DeepMind’s AI for protein structure is coming to the masses. Retrieved July 15, 2021, from https://www.nature.com/articles/d41586-021-01968-y
[2] Jumper et al., (2021). Highly accurate protein structure prediction with AlphaFold. Nature, https://doi.org/10.1038/s41586-021-03819-2.
[3] Baek, et al., (2021) Accurate prediction of protein structures and interactions using a three-track neural network. Science, https://doi.org/10.1126/science.abj8754.
[4] AlphaFold: a solution to a 50-year-old grand challenge in biology. Retrieved July 15, 2021, from https://deepmind.com/blog/article/alphafold-a-solution-to-a-50-year-old-grand-challenge-in-biology
[5] Accurate protein structure prediction now accessible to all. Retrieved July 15, 2021, from https://www.eurekalert.org/pub_releases/2021-07/uows-aps070921.php
蛋白質工程基于蛋白質的靈活性,通過人工手段改變氨基酸序列,實現對蛋白質結構和功能的修飾和改造。與基因組工程相比,蛋白質工程可直接對蛋白質分子進行操縱,借助突變的迭代積累,快速完成蛋白功能優化和創新。蛋......
根據《工業和信息化部辦公廳關于開展智能技術在生物制造領域典型應用案例征集工作的通知》(工信廳消費函〔2024〕394號),經省級工業和信息化主管部門推薦、形式審查及專家評價等程序,形成《人工智能在生物......
7月4日,在香港數碼港舉辦的“人工智能資助計劃”項目分享會上,人工智能資助計劃委員會主席冼漢迪披露,截至6月底,香港特區政府撥款30億港元的“人工智能資助計劃”已批出10個項目,研究范圍涵蓋本地大語言......
德國亥姆霍茲慕尼黑研究中心開發出一款名為“半人馬”(Centaur)的人工智能(AI)模型,能在幾乎所有心理學實驗中準確預測人類行為,甚至超越了科學家數十年來打造的傳統認知模型,堪稱“數字讀心術”。這......
德國亥姆霍茲慕尼黑研究中心開發出一款名為“半人馬”(Centaur)的人工智能(AI)模型,能在幾乎所有心理學實驗中準確預測人類行為,甚至超越了科學家數十年來打造的傳統認知模型,堪稱“數字讀心術”。這......
6月30日發表于《自然-人類行為》的一項研究指出,人類傾向于拒絕來自人工智能(AI)對話機器人的情緒支持,除非這種同理心被誤認為來自人類。生成式AI對話機器人,尤其是使用大語言模型(LLM)的對話機器......
6月30日發表于《自然-人類行為》的一項研究指出,人類傾向于拒絕來自人工智能(AI)對話機器人的情緒支持,除非這種同理心被誤認為來自人類。生成式AI對話機器人,尤其是使用大語言模型(LLM)的對話機器......
7月2至3日,在北京舉辦的2025全球數字經濟大會上,聯合國工業發展組織投資和技術促進辦公室聯合東壁科技數據有限責任公司(以下簡稱東壁科技數據)發布了全球科技文獻數據平臺dbdata.com(以下簡稱......
7月3日,在2025全球數字經濟大會人工智能融合應用發展論壇上,“楊梅工業”平臺正式發布上線并宣布開源。“楊梅工業”平臺是由北京工業軟件產業創新中心自主研發、專注于工業智能體開發與部署的平臺。該平臺秉......
7月3日,在2025全球數字經濟大會人工智能融合應用發展論壇上,“楊梅工業”平臺正式發布上線并宣布開源。“楊梅工業”平臺是由北京工業軟件產業創新中心自主研發、專注于工業智能體開發與部署的平臺。該平臺秉......